Método nuevo de inteligencia artificial ayuda a diseñar mejores medicamentos de anticuerpos contra la COVID-19
|
Por el equipo editorial de HospiMedica en español Actualizado el 21 Apr 2021 |

Ilustración
Los métodos de aprendizaje automático pueden ayudar a optimizar el desarrollo de medicamentos de anticuerpos contra la COVID-19, lo que lleva a sustancias activas con propiedades mejoradas, también con respecto a la tolerabilidad en el cuerpo, según los investigadores.
Los científicos de ETH Zúrich (Zúrich, Suiza) han desarrollado un método de aprendizaje automático que respalda la fase de optimización, lo que ayuda a desarrollar fármacos de anticuerpos más eficaces. Los anticuerpos no solo son producidos por nuestras células inmunes para combatir virus y otros patógenos en el cuerpo. Desde hace algunas décadas, la medicina también utiliza anticuerpos producidos por la biotecnología como fármacos. Esto se debe a que los anticuerpos son extremadamente buenos para unirse específicamente a estructuras moleculares de acuerdo con el principio de candado y llave. Su uso va desde la oncología hasta el tratamiento de enfermedades autoinmunes y afecciones neurodegenerativas.
Sin embargo, desarrollar tales fármacos con anticuerpos no es nada sencillo. El requisito básico es que un anticuerpo se una a su molécula diana de manera óptima. Al mismo tiempo, un fármaco de anticuerpos debe cumplir una serie de criterios adicionales. Por ejemplo, no debería desencadenar una respuesta inmunitaria en el cuerpo, debería ser eficiente para producir mediante biotecnología y debería permanecer estable durante un largo período de tiempo. Una vez que los científicos encuentran un anticuerpo que se une a la estructura molecular objetivo deseada, el proceso de desarrollo está lejos de terminar. Más bien, esto marca el comienzo de una fase en la que los investigadores utilizan la bioingeniería para tratar de mejorar las propiedades del anticuerpo.
Cuando los investigadores optimizan una molécula de anticuerpo completa en su forma terapéutica (es decir, no solo un fragmento de un anticuerpo), solía comenzar con un candidato principal de anticuerpo que se une razonablemente bien a la estructura objetivo deseada. Luego, los investigadores mutan aleatoriamente el gen que lleva el modelo del anticuerpo para producir algunos miles de candidatos de anticuerpos relacionados en el laboratorio. El siguiente paso es buscar entre ellos para encontrar los que mejor se unan a la estructura de destino. Los investigadores de ETH ahora utilizan el aprendizaje automático para aumentar el conjunto inicial de anticuerpos para ensayar a varios millones.
Los investigadores proporcionaron la prueba de concepto para su nuevo método utilizando la Herceptina, un medicamento anticanceroso de Roche, que ha estado en el mercado durante 20 años. A partir de la secuencia de ADN del anticuerpo Herceptina, los investigadores de ETH crearon alrededor de 40.000 anticuerpos relacionados utilizando un método de mutación CRISPR que habían desarrollado hace unos años. Los experimentos mostraron que 10.000 de ellos se unieron bien a la proteína diana en cuestión, una proteína específica de la superficie celular. Los científicos utilizaron las secuencias de ADN de estos 40.000 anticuerpos para entrenar un algoritmo de aprendizaje automático. Luego aplicaron el algoritmo entrenado para buscar en una base de datos de 70 millones de posibles secuencias de ADN de anticuerpos. Para estos 70 millones de candidatos, el algoritmo predijo qué tan bien se unirían los anticuerpos correspondientes a la proteína diana, lo que resultó en una lista de millones de secuencias que se espera se unirían.
Utilizando más modelos informáticos, los científicos predijeron qué tan bien estos millones de secuencias cumplirían los criterios adicionales para el desarrollo de medicamentos (tolerancia, producción, propiedades físicas). Esto redujo el número de secuencias candidatas a 8.000. De la lista de secuencias candidatas optimizadas en su computadora, los científicos seleccionaron 55 secuencias de las cuales podrían producir anticuerpos en el laboratorio y caracterizar sus propiedades. Experimentos posteriores demostraron que varios de ellos se unían incluso mejor a la proteína diana que la propia Herceptina, además de ser más fáciles de producir y más estables que la Herceptina. Los científicos de ETH ahora aplicarán su método de IA para optimizar los medicamentos de anticuerpos que se encuentran en desarrollo clínico.
“Con los procesos automatizados, pueden ensayar varios miles de candidatos terapéuticos en un laboratorio. Pero no es realmente factible evaluar más que eso”, dijo Sai Reddy, profesor del Departamento de Ciencia e Ingeniería de Biosistemas de ETH Zúrich, quien dirigió el estudio. “Por lo general, la mejor docena de anticuerpos de este examen pasan al siguiente paso y se analizan para determinar qué tan bien cumplen con los criterios adicionales. En última instancia, este método permite identificar el mejor anticuerpo de un grupo de unos pocos miles”.
Enlace relacionado:
ETH Zúrich
Los científicos de ETH Zúrich (Zúrich, Suiza) han desarrollado un método de aprendizaje automático que respalda la fase de optimización, lo que ayuda a desarrollar fármacos de anticuerpos más eficaces. Los anticuerpos no solo son producidos por nuestras células inmunes para combatir virus y otros patógenos en el cuerpo. Desde hace algunas décadas, la medicina también utiliza anticuerpos producidos por la biotecnología como fármacos. Esto se debe a que los anticuerpos son extremadamente buenos para unirse específicamente a estructuras moleculares de acuerdo con el principio de candado y llave. Su uso va desde la oncología hasta el tratamiento de enfermedades autoinmunes y afecciones neurodegenerativas.
Sin embargo, desarrollar tales fármacos con anticuerpos no es nada sencillo. El requisito básico es que un anticuerpo se una a su molécula diana de manera óptima. Al mismo tiempo, un fármaco de anticuerpos debe cumplir una serie de criterios adicionales. Por ejemplo, no debería desencadenar una respuesta inmunitaria en el cuerpo, debería ser eficiente para producir mediante biotecnología y debería permanecer estable durante un largo período de tiempo. Una vez que los científicos encuentran un anticuerpo que se une a la estructura molecular objetivo deseada, el proceso de desarrollo está lejos de terminar. Más bien, esto marca el comienzo de una fase en la que los investigadores utilizan la bioingeniería para tratar de mejorar las propiedades del anticuerpo.
Cuando los investigadores optimizan una molécula de anticuerpo completa en su forma terapéutica (es decir, no solo un fragmento de un anticuerpo), solía comenzar con un candidato principal de anticuerpo que se une razonablemente bien a la estructura objetivo deseada. Luego, los investigadores mutan aleatoriamente el gen que lleva el modelo del anticuerpo para producir algunos miles de candidatos de anticuerpos relacionados en el laboratorio. El siguiente paso es buscar entre ellos para encontrar los que mejor se unan a la estructura de destino. Los investigadores de ETH ahora utilizan el aprendizaje automático para aumentar el conjunto inicial de anticuerpos para ensayar a varios millones.
Los investigadores proporcionaron la prueba de concepto para su nuevo método utilizando la Herceptina, un medicamento anticanceroso de Roche, que ha estado en el mercado durante 20 años. A partir de la secuencia de ADN del anticuerpo Herceptina, los investigadores de ETH crearon alrededor de 40.000 anticuerpos relacionados utilizando un método de mutación CRISPR que habían desarrollado hace unos años. Los experimentos mostraron que 10.000 de ellos se unieron bien a la proteína diana en cuestión, una proteína específica de la superficie celular. Los científicos utilizaron las secuencias de ADN de estos 40.000 anticuerpos para entrenar un algoritmo de aprendizaje automático. Luego aplicaron el algoritmo entrenado para buscar en una base de datos de 70 millones de posibles secuencias de ADN de anticuerpos. Para estos 70 millones de candidatos, el algoritmo predijo qué tan bien se unirían los anticuerpos correspondientes a la proteína diana, lo que resultó en una lista de millones de secuencias que se espera se unirían.
Utilizando más modelos informáticos, los científicos predijeron qué tan bien estos millones de secuencias cumplirían los criterios adicionales para el desarrollo de medicamentos (tolerancia, producción, propiedades físicas). Esto redujo el número de secuencias candidatas a 8.000. De la lista de secuencias candidatas optimizadas en su computadora, los científicos seleccionaron 55 secuencias de las cuales podrían producir anticuerpos en el laboratorio y caracterizar sus propiedades. Experimentos posteriores demostraron que varios de ellos se unían incluso mejor a la proteína diana que la propia Herceptina, además de ser más fáciles de producir y más estables que la Herceptina. Los científicos de ETH ahora aplicarán su método de IA para optimizar los medicamentos de anticuerpos que se encuentran en desarrollo clínico.
“Con los procesos automatizados, pueden ensayar varios miles de candidatos terapéuticos en un laboratorio. Pero no es realmente factible evaluar más que eso”, dijo Sai Reddy, profesor del Departamento de Ciencia e Ingeniería de Biosistemas de ETH Zúrich, quien dirigió el estudio. “Por lo general, la mejor docena de anticuerpos de este examen pasan al siguiente paso y se analizan para determinar qué tan bien cumplen con los criterios adicionales. En última instancia, este método permite identificar el mejor anticuerpo de un grupo de unos pocos miles”.
Enlace relacionado:
ETH Zúrich
Últimas COVID-19 noticias
- Sistema de bajo costo detecta el virus SARS-CoV-2 en el aire del hospital mediante burbujas de alta tecnología
- China aprueba la primera vacuna inhalable contra la COVID-19 del mundo
- Vacuna en parche contra la COVID-19 combate variantes del SARS-CoV-2 mejor que las agujas
- Pruebas de viscosidad sanguínea predicen riesgo de muerte en pacientes hospitalizados con COVID-19
- ‘Computadora Covid’ usa IA para detectar COVID-19 en exámenes de TC de tórax
- Técnica de resonancia magnética muestra la causa de los síntomas de COVID prolongada
- TC del tórax de los pacientes con COVID-19 podrían ayudar a diferenciar entre las variantes del SARS-CoV-2
- Resonancia magnética especializada detecta anormalidades pulmonares en pacientes no hospitalizados con COVID prolongada
- Algoritmo de IA identifica a los pacientes hospitalizados con mayor riesgo de morir por COVID-19
- Estudio evalúa el impacto de la COVID-19 sobre la gammagrafía de ventilación/perfusión
- Sensor de sudor detecta biomarcadores claves que suministran una alarma precoz de la COVID-19 y la influenza
- Modelo de IA para seguimiento de COVID-19 predice mortalidad durante los primeros 30 días del ingreso
- ECG puede señalar pacientes hospitalizados con COVID-19 con riesgo más alto de muerte
- IA predice pronóstico de COVID a un nivel casi experto con base en tomografías computarizadas
- Examen de TC muestra evidencia de daño pulmonar persistente mucho tiempo después de neumonía por COVID-19
- Plataforma órgano-en-un-chip ayuda a diseñar estrategia para tratar complicaciones severas de la COVID-19
Canales
Cuidados Criticos
ver canal
Nueva tecnología podría revolucionar atención de valvulopatías cardíacas
La valvulopatía, que afecta la función de cualquiera de las cuatro válvulas del corazón, impacta al 2,5 % de la población estadounidense y al 13 % de las personas de... Más
Dispositivo electrónico portátil súper permeable permite monitorear bioseñales a largo plazo
Los dispositivos electrónicos portátiles se han convertido en una parte integral de la mejora de la salud y el estado físico al ofrecer un seguimiento continuo de señales f... Más
Nuevo hidrogel con capacidades mejoradas para tratar aneurismas y detener su progresión
Los aneurismas pueden desarrollarse en vasos sanguíneos de diferentes áreas del cuerpo, a menudo como resultado de aterosclerosis, infecciones, enfermedades inflamatorias y otros factores de riesgo.... MásNueva herramienta de IA predice eventos médicos para respaldar toma de decisiones clínicas en entornos de atención médica
En un nuevo estudio, los investigadores han demostrado el potencial de una nueva herramienta de inteligencia artificial (IA) para pronosticar la trayectoria de salud de un paciente mediante la predicción... MásTécnicas Quirúrgicas
ver canal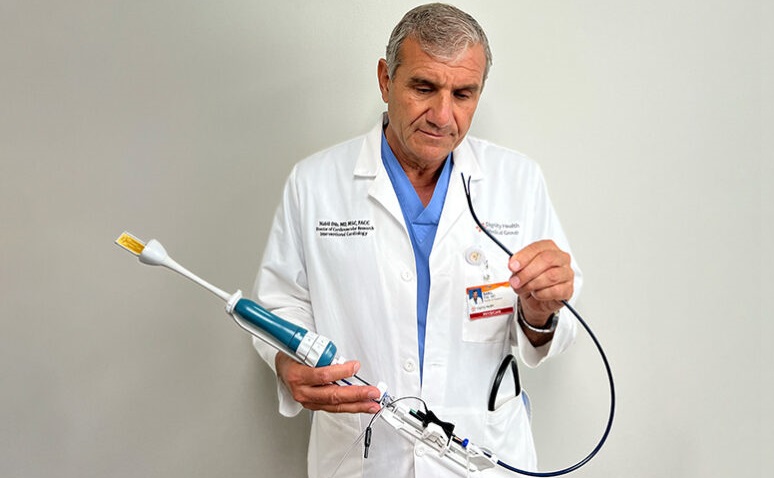
Nuevo sistema de catéter permite procedimientos transeptales más seguros y rentables
En 2021, los cardiólogos realizaron alrededor de 375.000 procedimientos transeptales del corazón izquierdo en los EUA, incluidos cierres, valvuloplastia, reparaciones, septostomías... Más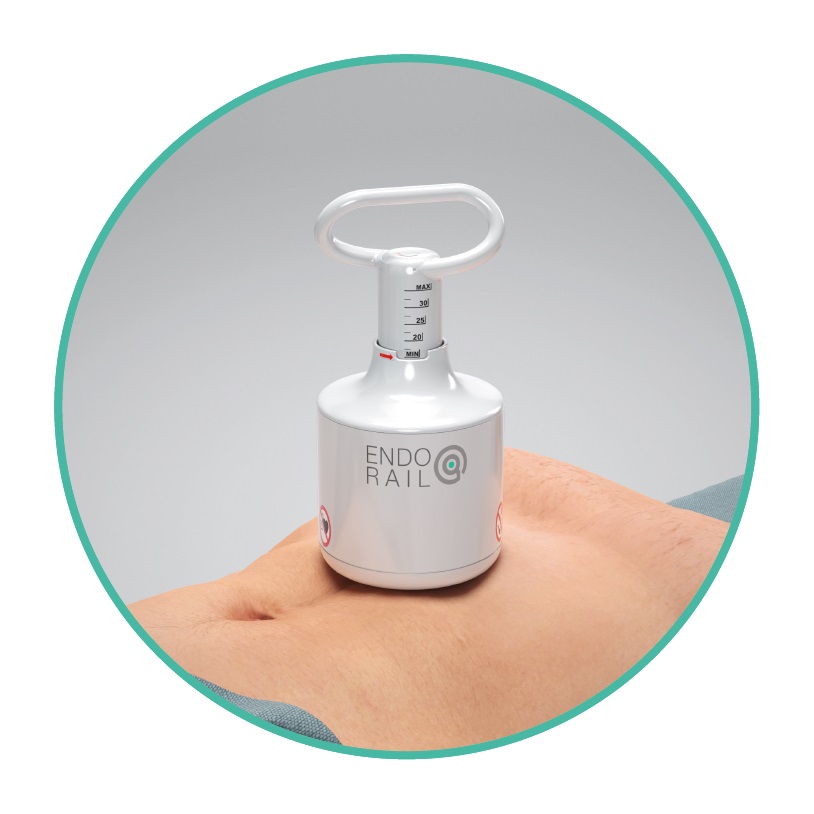
Tecnología de balón magnético optimiza resultados del procedimiento de colonoscopia
La colonoscopia es un procedimiento clave para diagnosticar, monitorear, prevenir y tratar diversas afecciones del colon, como el cáncer colorrectal y las enfermedades inflamatorias intestinales... Más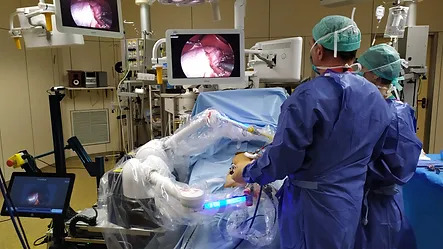
Sistema de cirugía robótica con capacidad basada en visión por computadora allana el camino para laparoscopia de próxima generación
La laparoscopia es una técnica quirúrgica en la que los cirujanos operan a través de pequeñas incisiones con una cámara interna e instrumentos. Ahora, una novedosa t... MásCuidados de Pacientes
ver canal
Solución de optimización de la capacidad quirúrgica ayuda a hospitales a impulsar utilización de quirófanos
Una solución innovadora tiene la capacidad de transformar la utilización de la capacidad quirúrgica al atacar la causa raíz de las ineficiencias los bloques de tiempo quirúrgico.... Más
Innovación revolucionaria en esterilización de instrumentos quirúrgicos mejora significativamente rendimiento del quirófano
Una innovación revolucionaria permite a los hospitales mejorar significativamente el tiempo de procesamiento de instrumentos y el rendimiento en quirófanos y departamentos de procesamiento... Más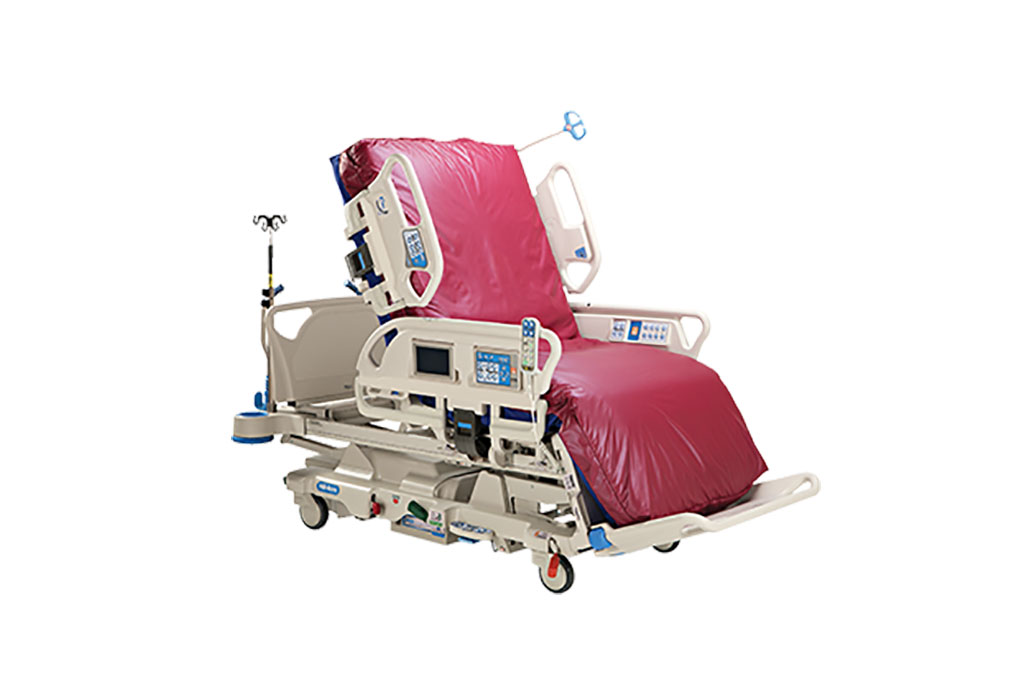
Cama para UCI de próxima generación ayuda a abordar necesidades complejas de cuidados intensivos
A medida que el entorno de cuidados intensivos se vuelve cada vez más exigente y complejo debido a las cambiantes necesidades de los hospitales, existe una necesidad apremiante de innovaciones que... MásTI
ver canal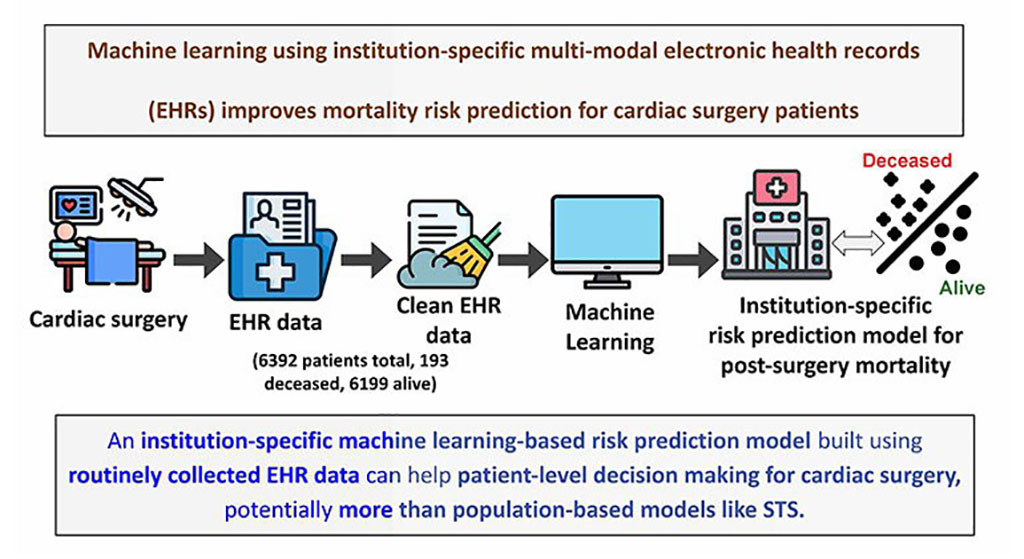
Modelo de aprendizaje automático mejora predicción del riesgo de mortalidad para pacientes de cirugía cardíaca
Se han implementado algoritmos de aprendizaje automático para crear modelos predictivos en varios campos médicos, y algunos han demostrado mejores resultados en comparación con sus... Más
Colaboración estratégica para desarrollar e integrar IA generativa en el cuidado de la salud
Los más altos expertos de la industria han subrayado el requisito inmediato de que los sistemas de salud y los hospitales respondan a las severas presiones de costos y márgenes.... MásPruebas POC
ver canal
Lector de inmunoensayo de pruebas POC proporciona análisis cuantitativo de kits de prueba para diagnóstico más preciso
Un lector de inmunoensayos cuantitativos pequeño y liviano que proporciona un análisis cuantitativo de cualquier tipo de kits o tiras de prueba rápida, y se puede conectar a una PC... Más
Sistema de hemostasia de sangre total POC de última generación reconoce necesidades específicas de servicios de emergencia y quirófanos
Las pruebas hemostáticas actuales proporcionan solo un subconjunto de la información necesaria, o tardan demasiado en ser útiles en situaciones críticas de hemorragia, lo que... Más
Laboratorio portátil permitirá identificación de infecciones bacterianas más rápida y económica en el punto de necesidad
La resistencia a los antimicrobianos (RAM) es la falta de respuesta de las bacterias a un determinado antibiótico debido a mutaciones o genes de resistencia que la especie ha adquirido.... MásNegocios
ver canal
Mindray adquirirá empresa china de dispositivos médicos APT Medical
Un reciente análisis exhaustivo de la industria ha demostrado que el mercado cardiovascular mundial ha alcanzado una valoración de 56 mil millones de dólares. En particular, el segmento... Más