Científicos identifican ocho “supervariantes” genéticas que aumentan el riesgo de morir por COVID-19
|
Por el equipo editorial de HospiMedica en español Actualizado el 16 Nov 2020 |
Ilustración
Los investigadores descubrieron un conjunto de ocho “supervariantes” genéticas que influyen fuertemente en el riesgo de mortalidad en pacientes con COVID-19.
El hallazgo fue realizado por investigadores del departamento de bioestadística de la Universidad de Yale (Nueva Haven, CT, EUA) a través de un estudio de asociación de genoma completo “mejorado” analíticamente (GWAS). Se ha descubierto que la gravedad de la COVID-19 es muy heterogénea y algunos pacientes no presentan síntomas mientras que otros quedan discapacitados o mueren. Además, los hombres y algunos grupos étnicos parecen tener un mayor riesgo de muerte por COVID-19, lo que implica que los factores genéticos del huésped pueden influir en el riesgo individual de muerte. Usando una nueva técnica de análisis potencialmente poderosa, los investigadores de Yale descubrieron la razón detrás de la fuerte variación en los resultados de los pacientes con COVID-19 incluso después de recibir un tratamiento idéntico.
Los investigadores primero buscaron variantes asociadas con la mortalidad a través de un GWAS utilizando datos de 1.778 pacientes infectados con SARS-CoV-2. De estos pacientes, el 25,03% (445) finalmente murió. Dado que el primer análisis no identificó variantes significativas, los investigadores de Yale adoptaron el concepto de supervariante para la detección de factores genéticos con el fin de mejorar el poder de la GWAS y tener en cuenta las posibles interacciones multiloci.
En el segundo tipo de análisis, los investigadores observaron más de 18.600.000 polimorfismos de un solo nucleótido (SNP), que representaban 146 muertes y 402 sobrevivientes. Mediante métodos de clasificación y agregación locales, identificaron las supervariantes significativas y luego aplicaron la técnica de bosque aleatorio para clasificar los SNP en términos de su importancia. Luego, el equipo pasó a agregar los mejores SNP de cada conjunto en supervariantes. Los investigadores adoptaron este enfoque ya que el desarrollo de COVID-19 está relacionado, tanto con la exposición ambiental como con la genética, aunque la genética podría tener una mayor influencia en la mortalidad. Además, dado que la COVID-19 es un síndrome complejo, los resultados pueden involucrar la interacción de múltiples factores genéticos.
Los investigadores descubrieron ocho “supervariantes” que se identificaron consistentemente en múltiples replicaciones como loci de susceptibilidad a la mortalidad por COVID-19. Según los investigadores, las supervariantes son “una combinación de alelos en múltiples loci análogos a un gen”. A diferencia de un gen, que representa una región específica en un cromosoma, los loci que contribuyen a una supervariante no están restringidos a ninguna ubicación particular en el genoma. Los investigadores descubrieron las supervariantes en los cromosomas 2, 6, 7, 8, 10, 16 y 17. Estos cromosomas contienen variantes y genes relacionados con disfunciones de los cilios (DNAH7 y CLUAP1), enfermedades cardiovasculares (DES y SPEG), enfermedades tromboembólicas (STXBP5), disfunciones mitocondriales (TOMM7) y función del sistema inmunológico innato (WSB1). Los investigadores esperan que estos hallazgos puedan proporcionar evidencia y pistas oportunas para una mejor comprensión de la patogénesis molecular de la COVID-19 y la base genética de la susceptibilidad heterogénea, con un impacto potencial en nuevas opciones terapéuticas.
Enlace relacionado:
Universidad de Yale
El hallazgo fue realizado por investigadores del departamento de bioestadística de la Universidad de Yale (Nueva Haven, CT, EUA) a través de un estudio de asociación de genoma completo “mejorado” analíticamente (GWAS). Se ha descubierto que la gravedad de la COVID-19 es muy heterogénea y algunos pacientes no presentan síntomas mientras que otros quedan discapacitados o mueren. Además, los hombres y algunos grupos étnicos parecen tener un mayor riesgo de muerte por COVID-19, lo que implica que los factores genéticos del huésped pueden influir en el riesgo individual de muerte. Usando una nueva técnica de análisis potencialmente poderosa, los investigadores de Yale descubrieron la razón detrás de la fuerte variación en los resultados de los pacientes con COVID-19 incluso después de recibir un tratamiento idéntico.
Los investigadores primero buscaron variantes asociadas con la mortalidad a través de un GWAS utilizando datos de 1.778 pacientes infectados con SARS-CoV-2. De estos pacientes, el 25,03% (445) finalmente murió. Dado que el primer análisis no identificó variantes significativas, los investigadores de Yale adoptaron el concepto de supervariante para la detección de factores genéticos con el fin de mejorar el poder de la GWAS y tener en cuenta las posibles interacciones multiloci.
En el segundo tipo de análisis, los investigadores observaron más de 18.600.000 polimorfismos de un solo nucleótido (SNP), que representaban 146 muertes y 402 sobrevivientes. Mediante métodos de clasificación y agregación locales, identificaron las supervariantes significativas y luego aplicaron la técnica de bosque aleatorio para clasificar los SNP en términos de su importancia. Luego, el equipo pasó a agregar los mejores SNP de cada conjunto en supervariantes. Los investigadores adoptaron este enfoque ya que el desarrollo de COVID-19 está relacionado, tanto con la exposición ambiental como con la genética, aunque la genética podría tener una mayor influencia en la mortalidad. Además, dado que la COVID-19 es un síndrome complejo, los resultados pueden involucrar la interacción de múltiples factores genéticos.
Los investigadores descubrieron ocho “supervariantes” que se identificaron consistentemente en múltiples replicaciones como loci de susceptibilidad a la mortalidad por COVID-19. Según los investigadores, las supervariantes son “una combinación de alelos en múltiples loci análogos a un gen”. A diferencia de un gen, que representa una región específica en un cromosoma, los loci que contribuyen a una supervariante no están restringidos a ninguna ubicación particular en el genoma. Los investigadores descubrieron las supervariantes en los cromosomas 2, 6, 7, 8, 10, 16 y 17. Estos cromosomas contienen variantes y genes relacionados con disfunciones de los cilios (DNAH7 y CLUAP1), enfermedades cardiovasculares (DES y SPEG), enfermedades tromboembólicas (STXBP5), disfunciones mitocondriales (TOMM7) y función del sistema inmunológico innato (WSB1). Los investigadores esperan que estos hallazgos puedan proporcionar evidencia y pistas oportunas para una mejor comprensión de la patogénesis molecular de la COVID-19 y la base genética de la susceptibilidad heterogénea, con un impacto potencial en nuevas opciones terapéuticas.
Enlace relacionado:
Universidad de Yale
Últimas COVID-19 noticias
- Sistema de bajo costo detecta el virus SARS-CoV-2 en el aire del hospital mediante burbujas de alta tecnología
- China aprueba la primera vacuna inhalable contra la COVID-19 del mundo
- Vacuna en parche contra la COVID-19 combate variantes del SARS-CoV-2 mejor que las agujas
- Pruebas de viscosidad sanguínea predicen riesgo de muerte en pacientes hospitalizados con COVID-19
- ‘Computadora Covid’ usa IA para detectar COVID-19 en exámenes de TC de tórax
- Técnica de resonancia magnética muestra la causa de los síntomas de COVID prolongada
- TC del tórax de los pacientes con COVID-19 podrían ayudar a diferenciar entre las variantes del SARS-CoV-2
- Resonancia magnética especializada detecta anormalidades pulmonares en pacientes no hospitalizados con COVID prolongada
- Algoritmo de IA identifica a los pacientes hospitalizados con mayor riesgo de morir por COVID-19
- Estudio evalúa el impacto de la COVID-19 sobre la gammagrafía de ventilación/perfusión
- Sensor de sudor detecta biomarcadores claves que suministran una alarma precoz de la COVID-19 y la influenza
- Modelo de IA para seguimiento de COVID-19 predice mortalidad durante los primeros 30 días del ingreso
- ECG puede señalar pacientes hospitalizados con COVID-19 con riesgo más alto de muerte
- IA predice pronóstico de COVID a un nivel casi experto con base en tomografías computarizadas
- Examen de TC muestra evidencia de daño pulmonar persistente mucho tiempo después de neumonía por COVID-19
- Plataforma órgano-en-un-chip ayuda a diseñar estrategia para tratar complicaciones severas de la COVID-19
Canales
Cuidados Criticos
ver canal
Nueva tecnología podría revolucionar atención de valvulopatías cardíacas
La valvulopatía, que afecta la función de cualquiera de las cuatro válvulas del corazón, impacta al 2,5 % de la población estadounidense y al 13 % de las personas de... Más
Dispositivo electrónico portátil súper permeable permite monitorear bioseñales a largo plazo
Los dispositivos electrónicos portátiles se han convertido en una parte integral de la mejora de la salud y el estado físico al ofrecer un seguimiento continuo de señales f... Más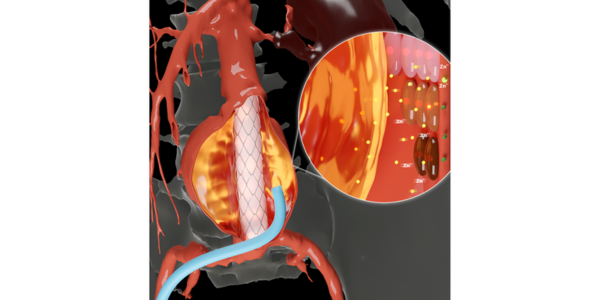
Nuevo hidrogel con capacidades mejoradas para tratar aneurismas y detener su progresión
Los aneurismas pueden desarrollarse en vasos sanguíneos de diferentes áreas del cuerpo, a menudo como resultado de aterosclerosis, infecciones, enfermedades inflamatorias y otros factores de riesgo.... MásNueva herramienta de IA predice eventos médicos para respaldar toma de decisiones clínicas en entornos de atención médica
En un nuevo estudio, los investigadores han demostrado el potencial de una nueva herramienta de inteligencia artificial (IA) para pronosticar la trayectoria de salud de un paciente mediante la predicción... MásTécnicas Quirúrgicas
ver canal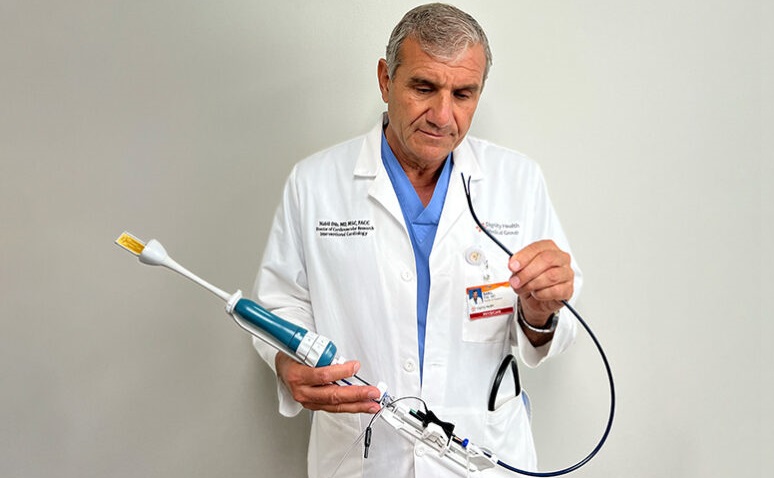
Nuevo sistema de catéter permite procedimientos transeptales más seguros y rentables
En 2021, los cardiólogos realizaron alrededor de 375.000 procedimientos transeptales del corazón izquierdo en los EUA, incluidos cierres, valvuloplastia, reparaciones, septostomías... Más
Tecnología de balón magnético optimiza resultados del procedimiento de colonoscopia
La colonoscopia es un procedimiento clave para diagnosticar, monitorear, prevenir y tratar diversas afecciones del colon, como el cáncer colorrectal y las enfermedades inflamatorias intestinales... Más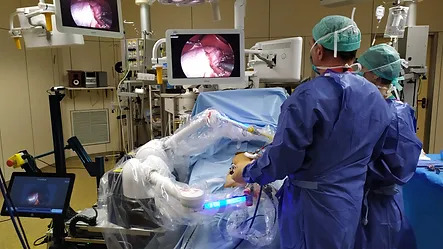
Sistema de cirugía robótica con capacidad basada en visión por computadora allana el camino para laparoscopia de próxima generación
La laparoscopia es una técnica quirúrgica en la que los cirujanos operan a través de pequeñas incisiones con una cámara interna e instrumentos. Ahora, una novedosa t... MásCuidados de Pacientes
ver canal
Solución de optimización de la capacidad quirúrgica ayuda a hospitales a impulsar utilización de quirófanos
Una solución innovadora tiene la capacidad de transformar la utilización de la capacidad quirúrgica al atacar la causa raíz de las ineficiencias los bloques de tiempo quirúrgico.... Más
Innovación revolucionaria en esterilización de instrumentos quirúrgicos mejora significativamente rendimiento del quirófano
Una innovación revolucionaria permite a los hospitales mejorar significativamente el tiempo de procesamiento de instrumentos y el rendimiento en quirófanos y departamentos de procesamiento... Más
Cama para UCI de próxima generación ayuda a abordar necesidades complejas de cuidados intensivos
A medida que el entorno de cuidados intensivos se vuelve cada vez más exigente y complejo debido a las cambiantes necesidades de los hospitales, existe una necesidad apremiante de innovaciones que... MásTI
ver canal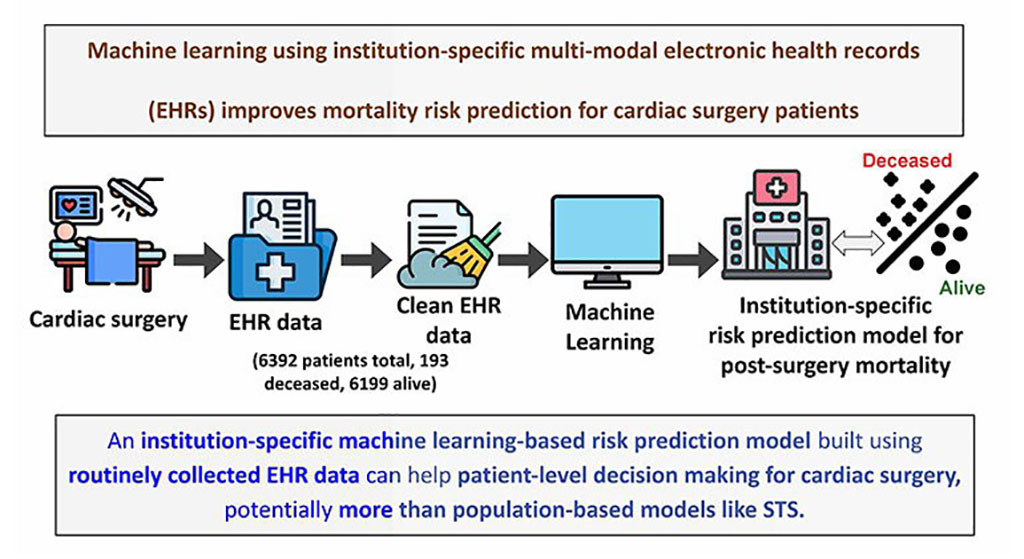
Modelo de aprendizaje automático mejora predicción del riesgo de mortalidad para pacientes de cirugía cardíaca
Se han implementado algoritmos de aprendizaje automático para crear modelos predictivos en varios campos médicos, y algunos han demostrado mejores resultados en comparación con sus... Más
Colaboración estratégica para desarrollar e integrar IA generativa en el cuidado de la salud
Los más altos expertos de la industria han subrayado el requisito inmediato de que los sistemas de salud y los hospitales respondan a las severas presiones de costos y márgenes.... MásPruebas POC
ver canal
Lector de inmunoensayo de pruebas POC proporciona análisis cuantitativo de kits de prueba para diagnóstico más preciso
Un lector de inmunoensayos cuantitativos pequeño y liviano que proporciona un análisis cuantitativo de cualquier tipo de kits o tiras de prueba rápida, y se puede conectar a una PC... Más
Sistema de hemostasia de sangre total POC de última generación reconoce necesidades específicas de servicios de emergencia y quirófanos
Las pruebas hemostáticas actuales proporcionan solo un subconjunto de la información necesaria, o tardan demasiado en ser útiles en situaciones críticas de hemorragia, lo que... Más
Laboratorio portátil permitirá identificación de infecciones bacterianas más rápida y económica en el punto de necesidad
La resistencia a los antimicrobianos (RAM) es la falta de respuesta de las bacterias a un determinado antibiótico debido a mutaciones o genes de resistencia que la especie ha adquirido.... MásNegocios
ver canal
Mindray adquirirá empresa china de dispositivos médicos APT Medical
Un reciente análisis exhaustivo de la industria ha demostrado que el mercado cardiovascular mundial ha alcanzado una valoración de 56 mil millones de dólares. En particular, el segmento... Más