Sistema de alerta temprana basado en la IA detecta las variantes del SARS-CoV-2 con potencial de alto riesgo
|
Por el equipo editorial de HospiMedica en español Actualizado el 17 Jan 2022 |

Ilustración
Un sistema de alerta temprana (SAE) combina el modelado estructural de la proteína Spike con inteligencia artificial (IA) para detectar y monitorear variantes de SARS-CoV-2 de alto riesgo, identificando >90 % de las variantes designadas por la Organización Mundial de la Salud (OMS), en promedio dos meses antes de recibir oficialmente la designación.
BioNTech SE (Maguncia, Alemania) e InstaDeep Ltd. (Londres, Reino Unido), desarrollaron un método computacional nuevo que analiza los datos de secuenciación disponibles en todo el mundo y predice variantes de alto riesgo del SARS-CoV-2. El SAE, desarrollado en colaboración por BioNTech e InstaDeep, se basa en métricas de aptitud y escape inmunológico calculadas por IA. El nuevo método combina el modelado estructural de la proteína viral Spike y los algoritmos de IA para señalar rápidamente las posibles variantes de alto riesgo ingresadas en los repositorios de datos de secuencia del SARS-CoV-2 en menos de un día en función de las métricas que califican su aptitud (por ejemplo, ACE2 y la interacción de la proteína Spike variante) así como sus propiedades de escape inmunológico.
El SAE se basa en dos enfoques: (1) el modelado estructural de la interacción del dominio de unión al receptor de la proteína Spike viral (RBD) con el receptor de la célula huésped y la puntuación del impacto de la variante del virus para poder escapar de la respuesta inmune y (2), modelado predictivo basado en IA para extraer información de cientos de miles de variantes de virus registradas de repositorios de secuencias globales. El SAE calcula una puntuación de escape inmune y una puntuación previa de aptitud (potencial de transmisibilidad). Si bien la puntuación de escape inmunitario por sí sola ya era altamente predictiva del riesgo, la combinación de estas dos métricas en una puntuación de Pareto proporcionó la mejor evaluación del riesgo que representa una variante de virus determinada. Cuanto más alto sea el puntaje, mayor será el riesgo de que la variante afecte la salud global. El enfoque de SAE clasifica las variantes del SARS-CoV-2 según el escape inmunológico y el potencial de aptitud basándose únicamente en los datos existentes y, por lo tanto, no depende de un enfoque de “esperar y observar”.
Las empresas validaron estas predicciones utilizando datos experimentales generados internamente y datos disponibles públicamente. Durante el período de prueba, el sistema identificó >90 % de las variantes designadas por la OMS (variantes preocupantes, VOC; variantes de interés, VOI; variantes bajo seguimiento, VUM) en promedio con dos meses de anticipación. El SAE detectó las variantes alfa, beta, gamma, theta, eta y ómicron, designadas por la OMS en la misma semana en que se cargó su secuencia por primera vez. La variante ómicron se clasificó como variante de alto riesgo el mismo día que su secuencia estuvo disponible. La variante IHU observada en Francia también fue evaluada por el SAE, que destacó las propiedades de escape inmunitario que son relativamente similares a ómicron, pero con una aptitud significativamente menor, por lo que es menos preocupante dados los datos actuales. Los resultados del estudio subrayan que el SAE es capaz de evaluar nuevas variantes en minutos y monitorear el riesgo de linajes de variantes casi en tiempo real. También es totalmente escalable a medida que se dispone de nuevos datos de variantes.
“Con los métodos computacionales avanzados que hemos desarrollado en los últimos meses, podemos analizar la información de la secuencia de la proteína Spike y clasificar las nuevas variantes de acuerdo con su escape inmunitario previsto y la puntuación de unión a la ACE2”, dijo Ugur Sahin, MD, director ejecutivo y cofundador de BioNTech. “La detección temprana de posibles variantes de alto riesgo podría ser una herramienta eficaz para alertar a los investigadores, los desarrolladores de vacunas, las autoridades sanitarias y los encargados de formular políticas, lo que brinda más tiempo para responder a las nuevas variantes de interés”.
“Actualmente, cada semana se descubren más de 10.000 secuencias variantes novedosas y los expertos humanos simplemente no pueden hacer frente a datos complejos a esta escala. Hemos abordado este desafío implementando las poderosas capacidades de inteligencia artificial de la plataforma DeepChain de InstaDeep, combinadas con el conocimiento y la tecnología del SARS-CoV-2 de BioNTech. Por primera vez, las variantes de alto riesgo podrían detectarse inmediatamente, lo que podría ahorrar meses de un tiempo precioso. Estamos felices de hacer que nuestro trabajo de investigación esté disponible públicamente y, lo que es más importante, esperamos su impacto continuo en el mundo real”, agregó Karim Beguir, cofundador y director ejecutivo de InstaDeep.
Enlace relacionado:
BioNTech SE
InstaDeep Ltd.
BioNTech SE (Maguncia, Alemania) e InstaDeep Ltd. (Londres, Reino Unido), desarrollaron un método computacional nuevo que analiza los datos de secuenciación disponibles en todo el mundo y predice variantes de alto riesgo del SARS-CoV-2. El SAE, desarrollado en colaboración por BioNTech e InstaDeep, se basa en métricas de aptitud y escape inmunológico calculadas por IA. El nuevo método combina el modelado estructural de la proteína viral Spike y los algoritmos de IA para señalar rápidamente las posibles variantes de alto riesgo ingresadas en los repositorios de datos de secuencia del SARS-CoV-2 en menos de un día en función de las métricas que califican su aptitud (por ejemplo, ACE2 y la interacción de la proteína Spike variante) así como sus propiedades de escape inmunológico.
El SAE se basa en dos enfoques: (1) el modelado estructural de la interacción del dominio de unión al receptor de la proteína Spike viral (RBD) con el receptor de la célula huésped y la puntuación del impacto de la variante del virus para poder escapar de la respuesta inmune y (2), modelado predictivo basado en IA para extraer información de cientos de miles de variantes de virus registradas de repositorios de secuencias globales. El SAE calcula una puntuación de escape inmune y una puntuación previa de aptitud (potencial de transmisibilidad). Si bien la puntuación de escape inmunitario por sí sola ya era altamente predictiva del riesgo, la combinación de estas dos métricas en una puntuación de Pareto proporcionó la mejor evaluación del riesgo que representa una variante de virus determinada. Cuanto más alto sea el puntaje, mayor será el riesgo de que la variante afecte la salud global. El enfoque de SAE clasifica las variantes del SARS-CoV-2 según el escape inmunológico y el potencial de aptitud basándose únicamente en los datos existentes y, por lo tanto, no depende de un enfoque de “esperar y observar”.
Las empresas validaron estas predicciones utilizando datos experimentales generados internamente y datos disponibles públicamente. Durante el período de prueba, el sistema identificó >90 % de las variantes designadas por la OMS (variantes preocupantes, VOC; variantes de interés, VOI; variantes bajo seguimiento, VUM) en promedio con dos meses de anticipación. El SAE detectó las variantes alfa, beta, gamma, theta, eta y ómicron, designadas por la OMS en la misma semana en que se cargó su secuencia por primera vez. La variante ómicron se clasificó como variante de alto riesgo el mismo día que su secuencia estuvo disponible. La variante IHU observada en Francia también fue evaluada por el SAE, que destacó las propiedades de escape inmunitario que son relativamente similares a ómicron, pero con una aptitud significativamente menor, por lo que es menos preocupante dados los datos actuales. Los resultados del estudio subrayan que el SAE es capaz de evaluar nuevas variantes en minutos y monitorear el riesgo de linajes de variantes casi en tiempo real. También es totalmente escalable a medida que se dispone de nuevos datos de variantes.
“Con los métodos computacionales avanzados que hemos desarrollado en los últimos meses, podemos analizar la información de la secuencia de la proteína Spike y clasificar las nuevas variantes de acuerdo con su escape inmunitario previsto y la puntuación de unión a la ACE2”, dijo Ugur Sahin, MD, director ejecutivo y cofundador de BioNTech. “La detección temprana de posibles variantes de alto riesgo podría ser una herramienta eficaz para alertar a los investigadores, los desarrolladores de vacunas, las autoridades sanitarias y los encargados de formular políticas, lo que brinda más tiempo para responder a las nuevas variantes de interés”.
“Actualmente, cada semana se descubren más de 10.000 secuencias variantes novedosas y los expertos humanos simplemente no pueden hacer frente a datos complejos a esta escala. Hemos abordado este desafío implementando las poderosas capacidades de inteligencia artificial de la plataforma DeepChain de InstaDeep, combinadas con el conocimiento y la tecnología del SARS-CoV-2 de BioNTech. Por primera vez, las variantes de alto riesgo podrían detectarse inmediatamente, lo que podría ahorrar meses de un tiempo precioso. Estamos felices de hacer que nuestro trabajo de investigación esté disponible públicamente y, lo que es más importante, esperamos su impacto continuo en el mundo real”, agregó Karim Beguir, cofundador y director ejecutivo de InstaDeep.
Enlace relacionado:
BioNTech SE
InstaDeep Ltd.
Últimas COVID-19 noticias
- Sistema de bajo costo detecta el virus SARS-CoV-2 en el aire del hospital mediante burbujas de alta tecnología
- China aprueba la primera vacuna inhalable contra la COVID-19 del mundo
- Vacuna en parche contra la COVID-19 combate variantes del SARS-CoV-2 mejor que las agujas
- Pruebas de viscosidad sanguínea predicen riesgo de muerte en pacientes hospitalizados con COVID-19
- ‘Computadora Covid’ usa IA para detectar COVID-19 en exámenes de TC de tórax
- Técnica de resonancia magnética muestra la causa de los síntomas de COVID prolongada
- TC del tórax de los pacientes con COVID-19 podrían ayudar a diferenciar entre las variantes del SARS-CoV-2
- Resonancia magnética especializada detecta anormalidades pulmonares en pacientes no hospitalizados con COVID prolongada
- Algoritmo de IA identifica a los pacientes hospitalizados con mayor riesgo de morir por COVID-19
- Estudio evalúa el impacto de la COVID-19 sobre la gammagrafía de ventilación/perfusión
- Sensor de sudor detecta biomarcadores claves que suministran una alarma precoz de la COVID-19 y la influenza
- Modelo de IA para seguimiento de COVID-19 predice mortalidad durante los primeros 30 días del ingreso
- ECG puede señalar pacientes hospitalizados con COVID-19 con riesgo más alto de muerte
- IA predice pronóstico de COVID a un nivel casi experto con base en tomografías computarizadas
- Examen de TC muestra evidencia de daño pulmonar persistente mucho tiempo después de neumonía por COVID-19
- Plataforma órgano-en-un-chip ayuda a diseñar estrategia para tratar complicaciones severas de la COVID-19
Canales
Cuidados Criticos
ver canal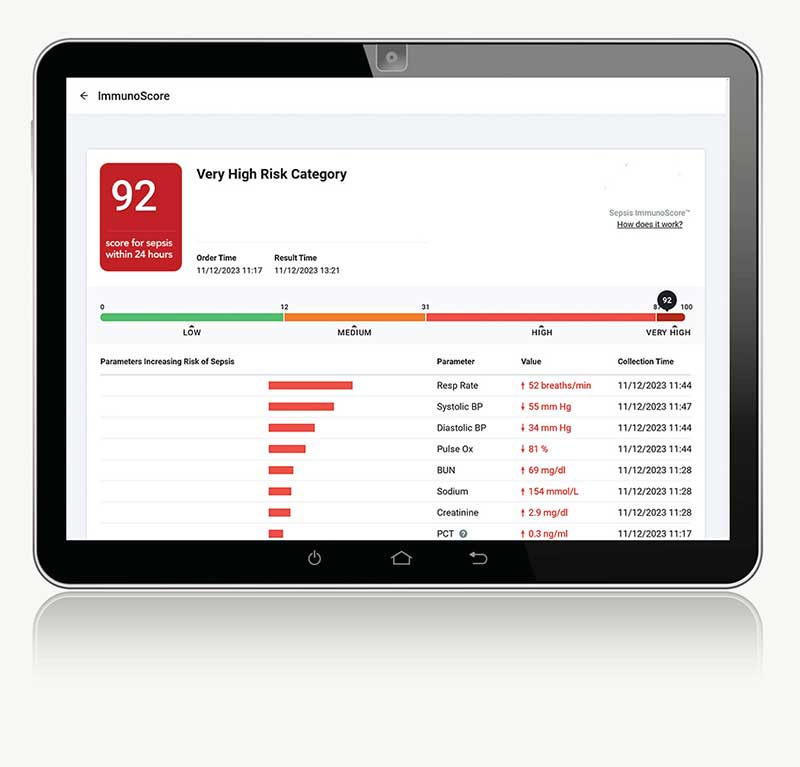
Herramienta de IA guía el diagnóstico rápido y la predicción de sepsis
La sepsis, una afección caracterizada por una respuesta inmune excesiva a la infección, presenta un desafío diagnóstico formidable, con implicaciones significativas para la... Más
La revascularización mejora la calidad de vida de pacientes con isquemia crónica que amenaza las extremidades
Más de 200 millones de personas en todo el mundo padecen enfermedad arterial periférica (EAP), una afección caracterizada por el estrechamiento de las arterias de las extremidades... MásTécnicas Quirúrgicas
ver canal
Primera sonda microscópica del mundo revolucionará el diagnóstico temprano del cáncer
En las primeras etapas del cáncer, las células son significativamente más blandas que las células normales, lo que facilita su movimiento a través de espacios pequeños... Más
El estimulador cerebral implantable más pequeño del mundo demostrado en paciente humano
Los dispositivos implantables que administran estimulación eléctrica al sistema nervioso central o periférico se emplean cada vez más en el tratamiento de afecciones psiqui... MásCuidados de Pacientes
ver canal
Solución de optimización de la capacidad quirúrgica ayuda a hospitales a impulsar utilización de quirófanos
Una solución innovadora tiene la capacidad de transformar la utilización de la capacidad quirúrgica al atacar la causa raíz de las ineficiencias los bloques de tiempo quirúrgico.... Más
Innovación revolucionaria en esterilización de instrumentos quirúrgicos mejora significativamente rendimiento del quirófano
Una innovación revolucionaria permite a los hospitales mejorar significativamente el tiempo de procesamiento de instrumentos y el rendimiento en quirófanos y departamentos de procesamiento... Más
Cama para UCI de próxima generación ayuda a abordar necesidades complejas de cuidados intensivos
A medida que el entorno de cuidados intensivos se vuelve cada vez más exigente y complejo debido a las cambiantes necesidades de los hospitales, existe una necesidad apremiante de innovaciones que... MásTI
ver canal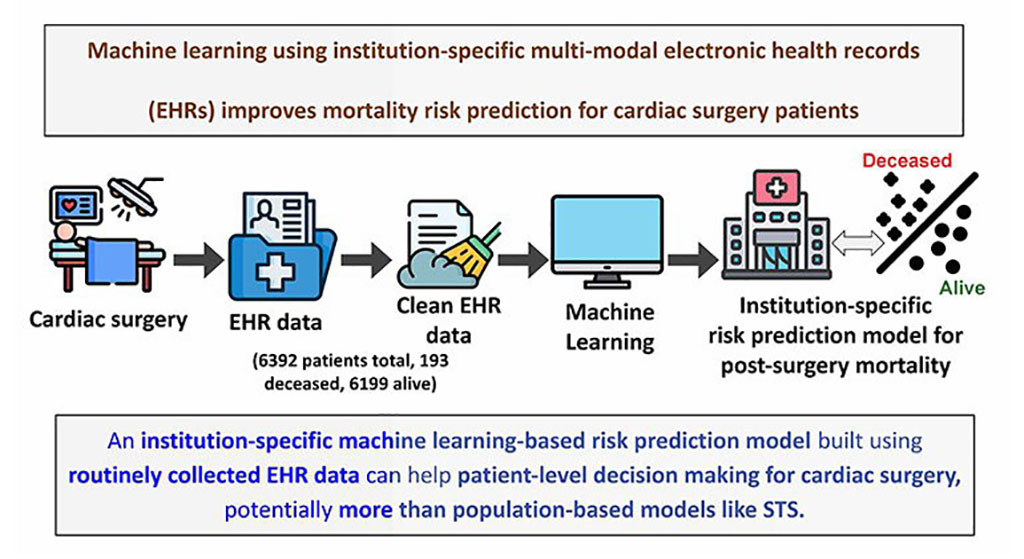
Modelo de aprendizaje automático mejora predicción del riesgo de mortalidad para pacientes de cirugía cardíaca
Se han implementado algoritmos de aprendizaje automático para crear modelos predictivos en varios campos médicos, y algunos han demostrado mejores resultados en comparación con sus... Más
Colaboración estratégica para desarrollar e integrar IA generativa en el cuidado de la salud
Los más altos expertos de la industria han subrayado el requisito inmediato de que los sistemas de salud y los hospitales respondan a las severas presiones de costos y márgenes.... MásPruebas POC
ver canal
Lector de inmunoensayo de pruebas POC proporciona análisis cuantitativo de kits de prueba para diagnóstico más preciso
Un lector de inmunoensayos cuantitativos pequeño y liviano que proporciona un análisis cuantitativo de cualquier tipo de kits o tiras de prueba rápida, y se puede conectar a una PC... Más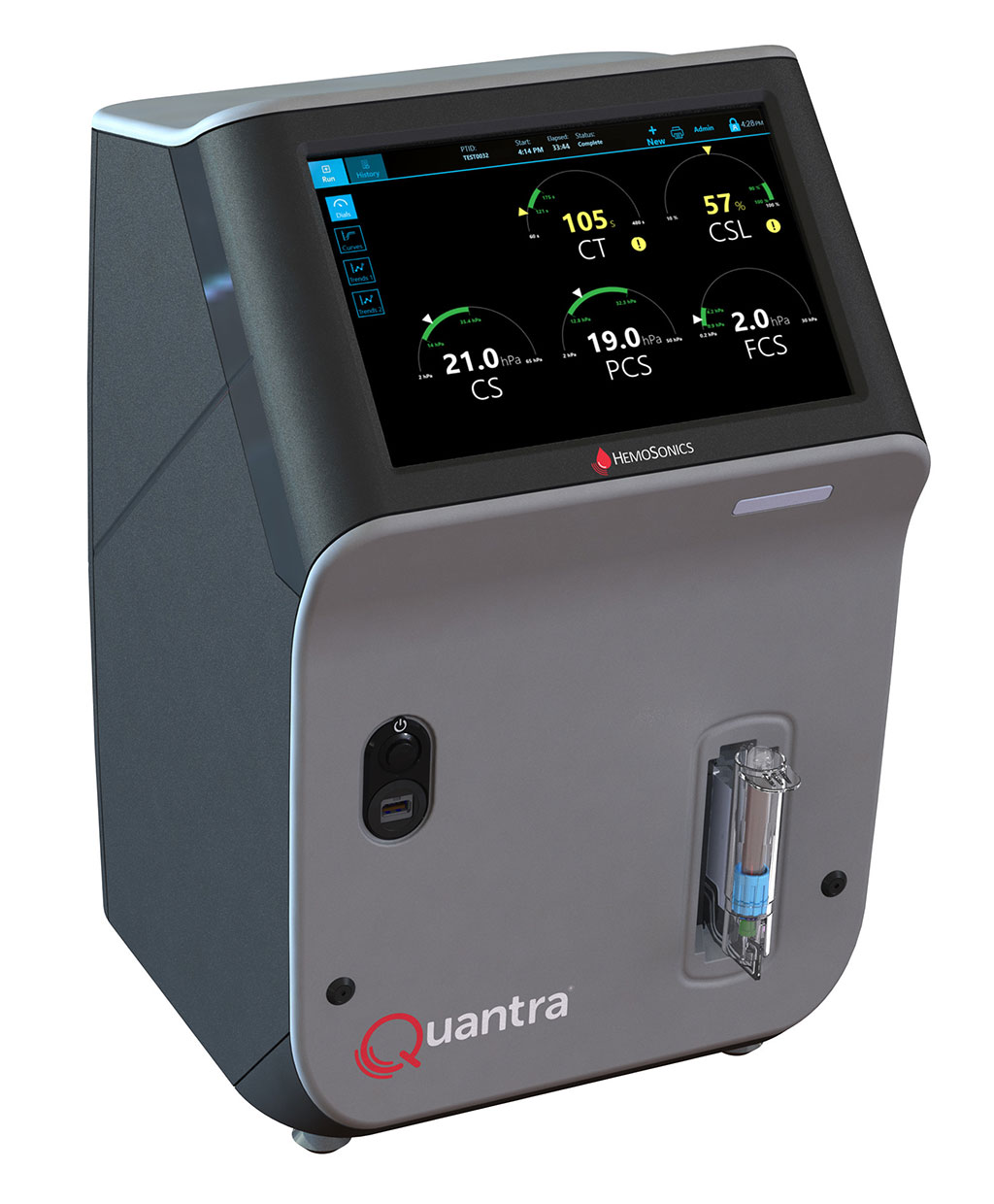
Sistema de hemostasia de sangre total POC de última generación reconoce necesidades específicas de servicios de emergencia y quirófanos
Las pruebas hemostáticas actuales proporcionan solo un subconjunto de la información necesaria, o tardan demasiado en ser útiles en situaciones críticas de hemorragia, lo que... Más
Laboratorio portátil permitirá identificación de infecciones bacterianas más rápida y económica en el punto de necesidad
La resistencia a los antimicrobianos (RAM) es la falta de respuesta de las bacterias a un determinado antibiótico debido a mutaciones o genes de resistencia que la especie ha adquirido.... MásNegocios
ver canal
Johnson & Johnson adquiere la empresa de dispositivos médicos cardiovasculares Shockwave Medical
Johnson & Johnson (New Brunswick, Nueva Jersey, EUA) y Shockwave Medical (Santa Clara, CA, EUA.) han firmado un acuerdo definitivo en virtud del cual Johnson & Johnson adquirirá todas las... Más