Herramienta nueva monitoriza las mutaciones del SARS-CoV-2 que dificultan el desarrollo de vacunas y medicamentos contra la COVID-19
|
Por el equipo editorial de HospiMedica en español Actualizado el 13 Sep 2020 |
Ilustración
Los científicos han desarrollado una nueva herramienta que contiene información sobre todas las estructuras de proteínas que coinciden con el genoma del SARS-CoV-2 (COVID-19), incluidas todas las mutaciones genéticas conocidas y la estructura de la proteína mutante resultante, para monitorear las mutaciones que dificultan el desarrollo de vacunas y medicamentos contra la COVID-19.
Asegurar que los tratamientos sigan efectivos a medida que el virus muta es un gran desafío para los investigadores. La nueva y poderosa herramienta desarrollada por científicos de la Universidad de Melbourne (Melbourne, Australia) aprovecha la información genómica y proteica sobre el virus y sus mutaciones para ayudar al desarrollo de vacunas y fármacos contra la COVID-19. Para desarrollar la herramienta de software y la biblioteca, denominada COVID-3D, el equipo analizó los datos de secuenciación del genoma de más de 120.000 muestras de SARS-CoV-2 de personas infectadas en todo el mundo, incluidas aquellas que afectan de manera única a Australia, para identificar mutaciones dentro de cada una de las proteínas del virus. Probaron y analizaron los efectos de las mutaciones en la estructura de sus proteínas mediante simulaciones por computadora. Estos datos se utilizaron para calcular todos los efectos biológicos de cada posible mutación dentro del genoma. Para ayudar a los investigadores a dar cuenta de posibles mutaciones futuras, el equipo analizó las mutaciones en los coronavirus relacionados, SARS-CoV y Bat RaTG13.
Las mutaciones o cambios en el material genético de un organismo son “errores” naturales en el proceso de replicación celular. Pueden darle al virus nuevos “poderes” de supervivencia, infectividad y virulencia. Afortunadamente, los investigadores encontraron que el SARS-CoV-2 muta más lentamente que otros virus como el de la influenza, con aproximadamente dos cambios nuevos en su genoma cada mes. La COVID-3D puede ayudar a los investigadores a reconocer cómo operan las mutaciones e identificar objetivos de vacunas y medicamentos más efectivos. Varias universidades e instituciones de investigación internacionales ya utilizan la COVID-3D en el desarrollo de vacunas y tratamientos.
“Aunque el virus SARS-CoV-2 es un patógeno relativamente nuevo, su capacidad para acumular mutaciones en sus genes fue evidente desde el comienzo de esta pandemia”, dijo el profesor asociado de la Universidad de Melbourne, David Ascher. “En el contexto del diseño y descubrimiento de fármacos terapéuticos, estas mutaciones y los patrones por los cuales se acumulan dentro de las estructuras proteicas del virus pueden afectar la capacidad de las vacunas y los fármacos para unirse al virus o para crear una respuesta inmunitaria específica contra él. Debido a esto, los científicos no solo deben intentar controlar el virus, sino ser más astutos al momento de predecir cómo cambiará con el tiempo”.
Enlace relacionado:
Universidad de Melbourne
Asegurar que los tratamientos sigan efectivos a medida que el virus muta es un gran desafío para los investigadores. La nueva y poderosa herramienta desarrollada por científicos de la Universidad de Melbourne (Melbourne, Australia) aprovecha la información genómica y proteica sobre el virus y sus mutaciones para ayudar al desarrollo de vacunas y fármacos contra la COVID-19. Para desarrollar la herramienta de software y la biblioteca, denominada COVID-3D, el equipo analizó los datos de secuenciación del genoma de más de 120.000 muestras de SARS-CoV-2 de personas infectadas en todo el mundo, incluidas aquellas que afectan de manera única a Australia, para identificar mutaciones dentro de cada una de las proteínas del virus. Probaron y analizaron los efectos de las mutaciones en la estructura de sus proteínas mediante simulaciones por computadora. Estos datos se utilizaron para calcular todos los efectos biológicos de cada posible mutación dentro del genoma. Para ayudar a los investigadores a dar cuenta de posibles mutaciones futuras, el equipo analizó las mutaciones en los coronavirus relacionados, SARS-CoV y Bat RaTG13.
Las mutaciones o cambios en el material genético de un organismo son “errores” naturales en el proceso de replicación celular. Pueden darle al virus nuevos “poderes” de supervivencia, infectividad y virulencia. Afortunadamente, los investigadores encontraron que el SARS-CoV-2 muta más lentamente que otros virus como el de la influenza, con aproximadamente dos cambios nuevos en su genoma cada mes. La COVID-3D puede ayudar a los investigadores a reconocer cómo operan las mutaciones e identificar objetivos de vacunas y medicamentos más efectivos. Varias universidades e instituciones de investigación internacionales ya utilizan la COVID-3D en el desarrollo de vacunas y tratamientos.
“Aunque el virus SARS-CoV-2 es un patógeno relativamente nuevo, su capacidad para acumular mutaciones en sus genes fue evidente desde el comienzo de esta pandemia”, dijo el profesor asociado de la Universidad de Melbourne, David Ascher. “En el contexto del diseño y descubrimiento de fármacos terapéuticos, estas mutaciones y los patrones por los cuales se acumulan dentro de las estructuras proteicas del virus pueden afectar la capacidad de las vacunas y los fármacos para unirse al virus o para crear una respuesta inmunitaria específica contra él. Debido a esto, los científicos no solo deben intentar controlar el virus, sino ser más astutos al momento de predecir cómo cambiará con el tiempo”.
Enlace relacionado:
Universidad de Melbourne
Últimas COVID-19 noticias
- Sistema de bajo costo detecta el virus SARS-CoV-2 en el aire del hospital mediante burbujas de alta tecnología
- China aprueba la primera vacuna inhalable contra la COVID-19 del mundo
- Vacuna en parche contra la COVID-19 combate variantes del SARS-CoV-2 mejor que las agujas
- Pruebas de viscosidad sanguínea predicen riesgo de muerte en pacientes hospitalizados con COVID-19
- ‘Computadora Covid’ usa IA para detectar COVID-19 en exámenes de TC de tórax
- Técnica de resonancia magnética muestra la causa de los síntomas de COVID prolongada
- TC del tórax de los pacientes con COVID-19 podrían ayudar a diferenciar entre las variantes del SARS-CoV-2
- Resonancia magnética especializada detecta anormalidades pulmonares en pacientes no hospitalizados con COVID prolongada
- Algoritmo de IA identifica a los pacientes hospitalizados con mayor riesgo de morir por COVID-19
- Estudio evalúa el impacto de la COVID-19 sobre la gammagrafía de ventilación/perfusión
- Sensor de sudor detecta biomarcadores claves que suministran una alarma precoz de la COVID-19 y la influenza
- Modelo de IA para seguimiento de COVID-19 predice mortalidad durante los primeros 30 días del ingreso
- ECG puede señalar pacientes hospitalizados con COVID-19 con riesgo más alto de muerte
- IA predice pronóstico de COVID a un nivel casi experto con base en tomografías computarizadas
- Examen de TC muestra evidencia de daño pulmonar persistente mucho tiempo después de neumonía por COVID-19
- Plataforma órgano-en-un-chip ayuda a diseñar estrategia para tratar complicaciones severas de la COVID-19
Canales
Cuidados Criticos
ver canal
Dispositivo electrónico portátil súper permeable permite monitorear bioseñales a largo plazo
Los dispositivos electrónicos portátiles se han convertido en una parte integral de la mejora de la salud y el estado físico al ofrecer un seguimiento continuo de señales f... Más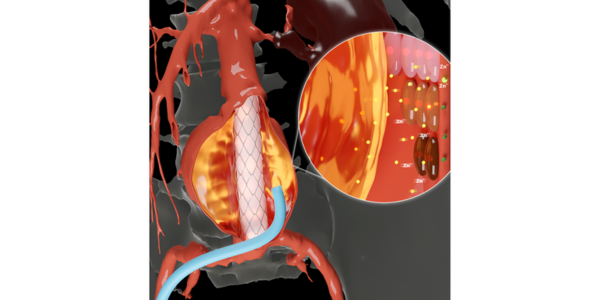
Nuevo hidrogel con capacidades mejoradas para tratar aneurismas y detener su progresión
Los aneurismas pueden desarrollarse en vasos sanguíneos de diferentes áreas del cuerpo, a menudo como resultado de aterosclerosis, infecciones, enfermedades inflamatorias y otros factores de riesgo.... MásNueva herramienta de IA predice eventos médicos para respaldar toma de decisiones clínicas en entornos de atención médica
En un nuevo estudio, los investigadores han demostrado el potencial de una nueva herramienta de inteligencia artificial (IA) para pronosticar la trayectoria de salud de un paciente mediante la predicción... Más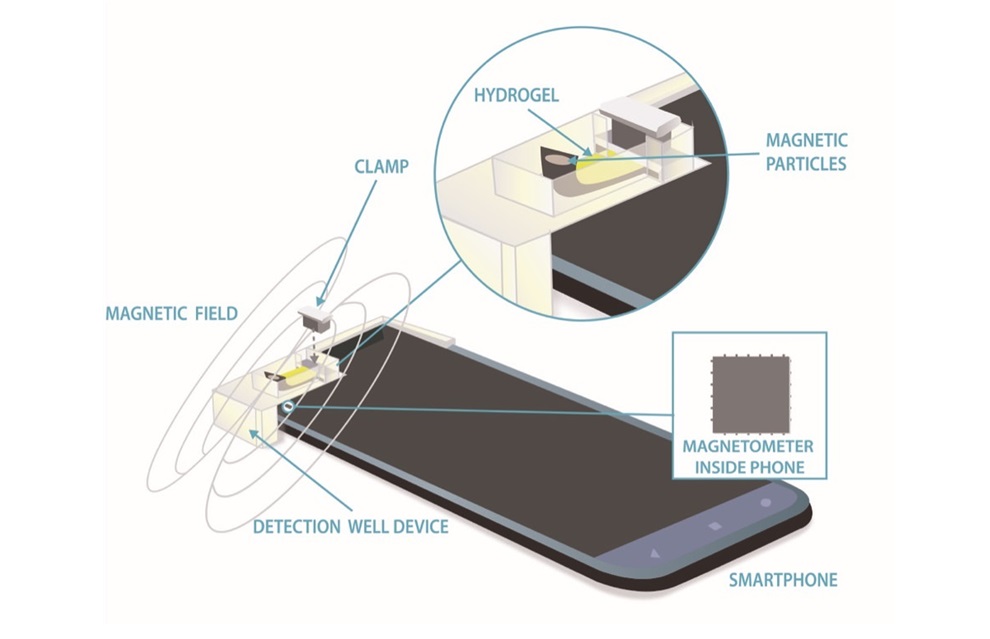
El magnetómetro de un teléfono inteligente utiliza hidrogel magnetizado para medir biomarcadores para el diagnóstico de enfermedades
Casi todos los teléfonos inteligentes modernos incorporan una brújula o un magnetómetro, que detecta el campo magnético de la Tierra, crucial para la navegación.... MásTécnicas Quirúrgicas
ver canal
Simple protocolo de prevención puede reducir infecciones peligrosas del sitio quirúrgico
Las infecciones del sitio quirúrgico (ISQ) representan un riesgo significativo en el sector de la salud, aumentando la probabilidad de muerte del paciente hasta 11 veces en comparación con... Más
Nuevos implantes inteligentes podrían monitorear continuamente y promover activamente la curación ósea
Los huesos poseen una combinación única de estabilidad y elasticidad; no sólo crecen y se renuevan, sino que también están diseñados para soportar una fuerza sustancial.... MásCuidados de Pacientes
ver canal
Solución de optimización de la capacidad quirúrgica ayuda a hospitales a impulsar utilización de quirófanos
Una solución innovadora tiene la capacidad de transformar la utilización de la capacidad quirúrgica al atacar la causa raíz de las ineficiencias los bloques de tiempo quirúrgico.... Más
Innovación revolucionaria en esterilización de instrumentos quirúrgicos mejora significativamente rendimiento del quirófano
Una innovación revolucionaria permite a los hospitales mejorar significativamente el tiempo de procesamiento de instrumentos y el rendimiento en quirófanos y departamentos de procesamiento... Más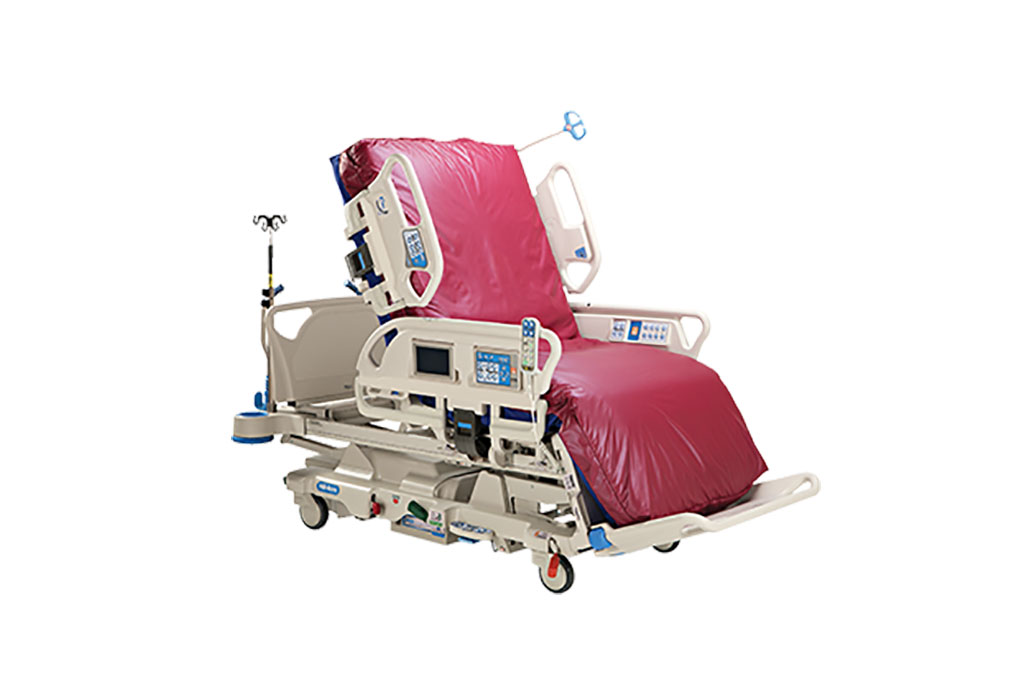
Cama para UCI de próxima generación ayuda a abordar necesidades complejas de cuidados intensivos
A medida que el entorno de cuidados intensivos se vuelve cada vez más exigente y complejo debido a las cambiantes necesidades de los hospitales, existe una necesidad apremiante de innovaciones que... MásTI
ver canal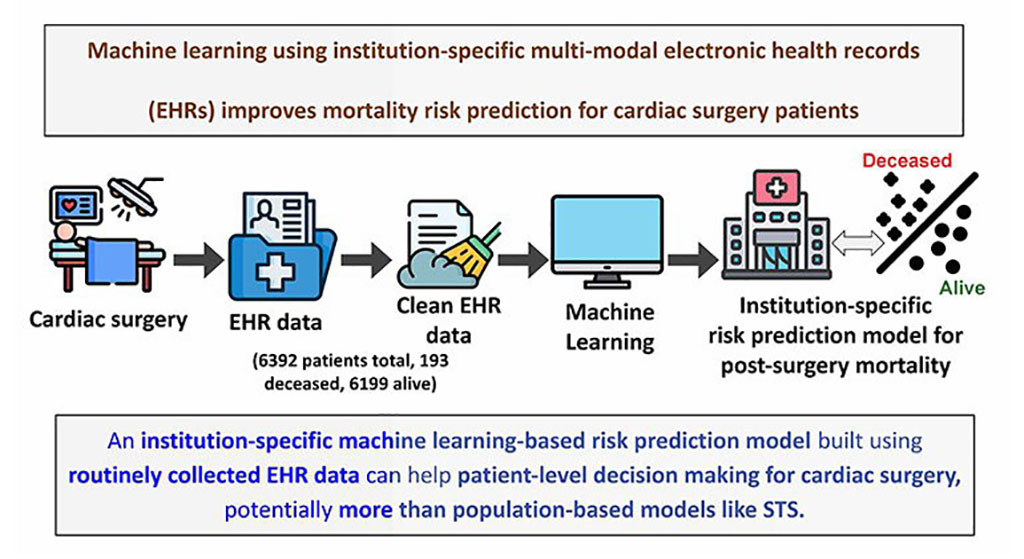
Modelo de aprendizaje automático mejora predicción del riesgo de mortalidad para pacientes de cirugía cardíaca
Se han implementado algoritmos de aprendizaje automático para crear modelos predictivos en varios campos médicos, y algunos han demostrado mejores resultados en comparación con sus... Más
Colaboración estratégica para desarrollar e integrar IA generativa en el cuidado de la salud
Los más altos expertos de la industria han subrayado el requisito inmediato de que los sistemas de salud y los hospitales respondan a las severas presiones de costos y márgenes.... MásPruebas POC
ver canal
Lector de inmunoensayo de pruebas POC proporciona análisis cuantitativo de kits de prueba para diagnóstico más preciso
Un lector de inmunoensayos cuantitativos pequeño y liviano que proporciona un análisis cuantitativo de cualquier tipo de kits o tiras de prueba rápida, y se puede conectar a una PC... Más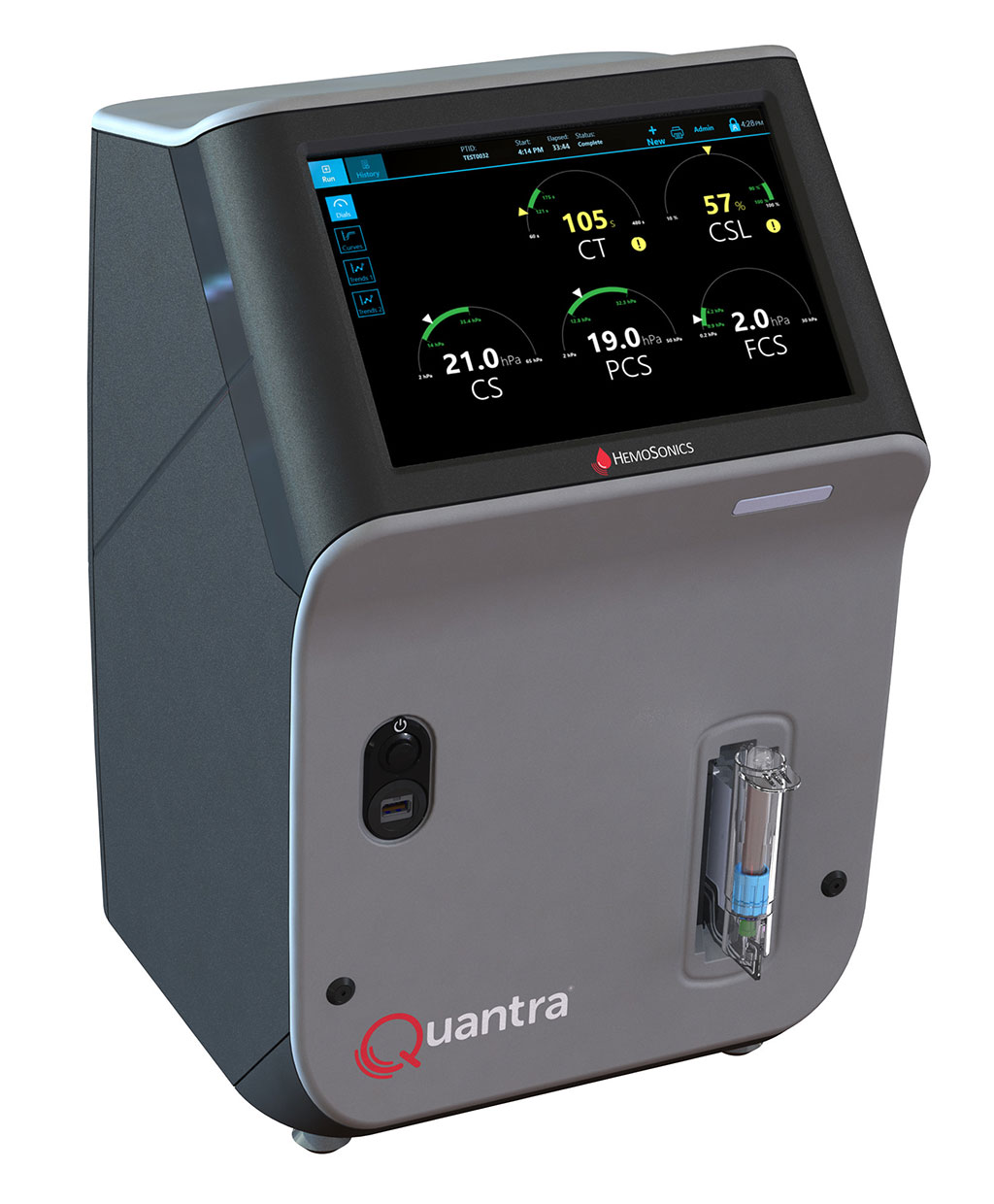
Sistema de hemostasia de sangre total POC de última generación reconoce necesidades específicas de servicios de emergencia y quirófanos
Las pruebas hemostáticas actuales proporcionan solo un subconjunto de la información necesaria, o tardan demasiado en ser útiles en situaciones críticas de hemorragia, lo que... Más
Laboratorio portátil permitirá identificación de infecciones bacterianas más rápida y económica en el punto de necesidad
La resistencia a los antimicrobianos (RAM) es la falta de respuesta de las bacterias a un determinado antibiótico debido a mutaciones o genes de resistencia que la especie ha adquirido.... MásNegocios
ver canal
Mindray adquirirá empresa china de dispositivos médicos APT Medical
Un reciente análisis exhaustivo de la industria ha demostrado que el mercado cardiovascular mundial ha alcanzado una valoración de 56 mil millones de dólares. En particular, el segmento... Más